欢迎关注”生信修炼手册”!
通常在分析peak区域对应的靶基因时,会选取转录起始位点TSS上下游一定长度的区域作为候选的靶基因范围,本文介绍下如何利用bedtools来对peak与TSS区域的overlap情况进行分析,从而得到靶基因,可以分为以下几步
1. 得到物种对应的TSS位点信息
以hg38为例,通过UCSC的FTP服务可以得到物种对应的refFlat文件,链接如下
http://hgdownload.soe.ucsc.edu/goldenPath/hg38/database/

refFLat和refGene这两个文件记录的信息相同,refFlat文件列数更少,这里我们选择下载refFlat.txt.gz, 该文件的内容如下所示
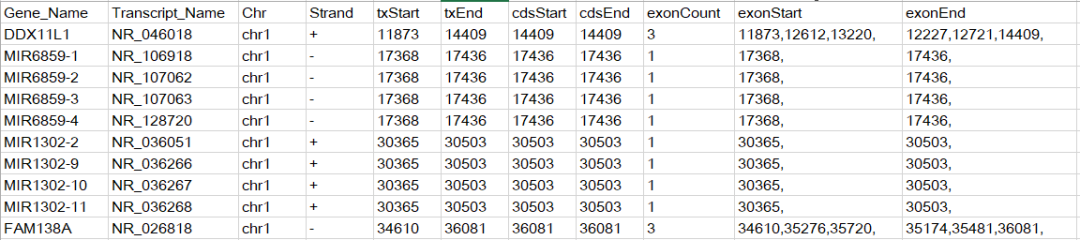
在原始文件中是没有第一行的标题的,我手动添加的标题是为了方便描述每列的含义,从该文件中可以得到TSS位点信息。
2. 整理TSS位点信息
bedtools要求输入的文件格式为bed, gff, vcf等,这里我们需要把上述下载的原始文件转换为bed格式,用法如下
awk '{print $3"\t"$5"\t"$5"\t"$2"\t"$1"\t"$4}' > hg38.tss.bed内容如下所示
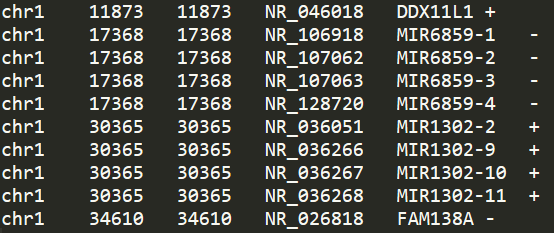
3. 运行bedtools window
bedtools windows和intersect的功能类似,都是用于求两个区间A和B的交集,只不过window会在A区间的上下游加上一个可以自定义的长度之后,再与B区间求交集,原理示意如下
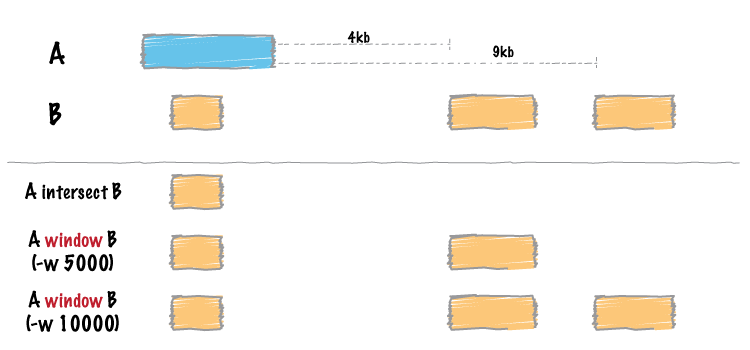
以TSS上下游5kb为例,用法如下
bedtools window -a hg39.tss.bed -b peak.bed -w 5000 -sm > overlap.txt通过window这个命令,可以灵活的定义TSS上下游的区间,快速得到peak对应的靶基因。
·end·
—如果喜欢,快分享给你的朋友们吧—
扫描关注微信号,更多精彩内容等着你!











